Encuentra más información en nuestro repositorio digital
El análisis de la metagenómica ha permitido medir la diversidad del microbioma en muestras ambientales sin un enriquecimiento dirigido previo. Los estudios funcionales y filogenéticos basados en la diversidad microbiana obtenidos utilizando plataformas HTS han avanzado desde la detección de organismos conocidos y el descubrimiento de especies desconocidas hasta las aplicaciones en el diagnóstico de enfermedades.
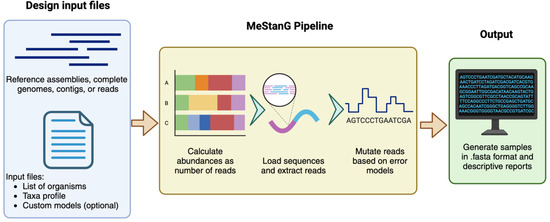
Unos procesos de validación sólidos son esenciales para la fiabilidad de los ensayos, ya que requieren muestras estándar y bases de datos derivadas de muestras reales y controles artificiales generados in silico. Proponemos un MeStanG como recurso para generar conjuntos de datos HTS Nanopore para evaluar las tuberías bioinformáticas actuales y emergentes. MeStanG permite diseñar muestras con abundancias de organismos definidas por el usuario expresadas como número de lecturas, secuencias de referencia y errores predeterminados o personalizados mediante perfiles de secuenciación.
La tubería del simulador se evaluó mediante el análisis de sus muestras metagenómicas simuladas de salida que contienen abundancias leídas conocidas utilizando cartografía de lectura, ensamblaje del genoma y clasificación taxonómica en tres escenarios: una comunidad bacteriana compuesta de nueve organismos diferentes, muestras similares a patógenos-plantas de trigo infectadas, y un muestreo por dilución en serie del patógeno viral. La evaluación fue capaz de reportar consistentemente los mismos organismos, y sus abundancias leídas según lo previsto en el diseño de muestra metagenómica.